Das BioSC Boost-Fund-Projekt „PectiLyse“ hatte das Ziel, für den Abbau von pektinreicher Biomasse den pilzlichen Modell-Organismus Ustilago maydis einzusetzen. Bei der Zuckerproduktion aus Zuckerrüben fallen große Mengen von organischen Seitenströmen an. Diese weisen einen hohen Gehalt des komplexen Polysaccharids Pektin auf. Bisher werden die pektinhaltigen Seitenströme mit geringer Wertschöpfung als Tierfutter verkauft. Im Projekt „PectiLyse“ sollten grundlegende Methoden etabliert werden, um in Zukunft aus diesen organischen Resten wertvollere Produkte in einem integrierten Bioprozess zu gewinnen.
Ein Konsortium von Forscherinnen und Forschern verschiedener Fachrichtungen erlaubte es dabei, die Fragestellung des Projektes interdisziplinär anzugehen: Mikrobiologen mit der Expertise für die genetische Manipulation des Pilzes sowie für die Produktion von organischen Säuren haben mit führenden Bioprozesstechnikern ein schlagkräftiges Team gebildet. Dies ermöglichte die Verfolgung eines ganzheitlichen Ansatzes, in dem optimierte Stämme effizient mittels Online-Analytik charakterisiert werden konnten.
Der Pilz Ustilago maydis besitzt einige Attribute, die ihn für die Entwicklung eines integrierten Bioprozesses besonders qualifizieren. Im Gegensatz zu anderen bekannten pektinabbauenden Pilzen kann Ustilago maydis nicht nur filamentös, sondern auch hefeartig wachsen. Dies bringt entscheidende Vorteile in der Handhabung und vor allem in der Kultivierung mit sich. Ustilago maydis infiziert in der Natur Maispflanzen und löst den sogenannten Beulenbrand aus. Für den Menschen ist er jedoch ungefährlich. Infizierte Maiskolben sind sogar für den menschlichen Konsum geeignet und werden in Mexiko als Delikatesse gehandelt. Hefeartig wachsende Laborstämme sind für Pflanzen nicht infektiös und eignen sich hervorragend für die Biotechnologie.
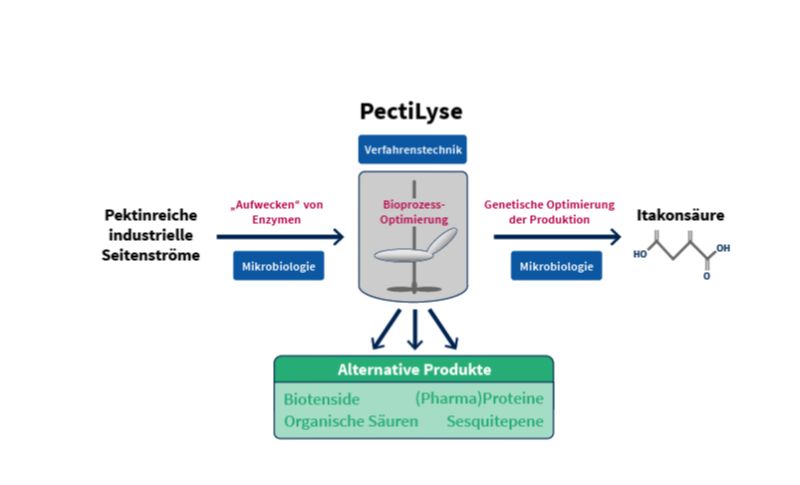
Aufwertung pektinreicher industrieller Seitenströme in einem nachhaltigen mikrobiellen Bioprozess
Copyright: Institut für Mikrobiologie, HHU Düsseldorf
Die Eigenschaft des Pflanzenpathogens spiegelt sich im Enzymrepertoire von Ustilago maydis wider: Im Gegensatz zu anderen Modellpilzen wie der Bäckerhefe besitzt Ustilago maydis bereits Enzyme für die Verstoffwechslung vieler in Pektin enthaltener Einzelzucker. Zudem existieren weitere Enzyme, die für den Pektinabbau in diese Einzelzucker von Nutzen sind. Leider werden diese nur in der infektiösen Phase während der Maisbesiedlung gebildet. Um dieses Problem zu umgehen, wurden die entsprechenden Enzyme durch molekularbiologische Veränderungen quasi aufgeweckt und damit aktiviert. Mithilfe dieses „sleeping beauty“-Prinzips konnten die gewünschten Enzyme nun auch erfolgreich in der Hefe-Phase produziert und aus der Zelle ausgeschleust werden. Dies ermöglicht eine Ausweitung des Substratspektrums.
Komplexes Molekül spalten
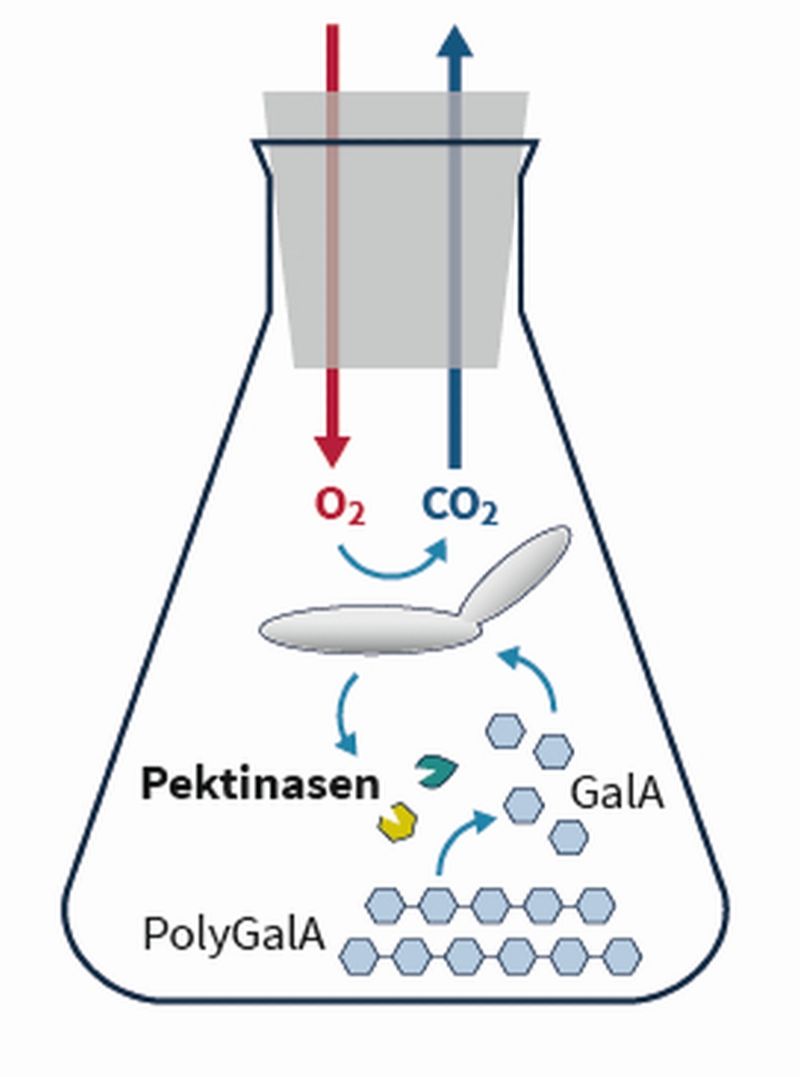
Der Hauptbestandteil von Pektin ist die Polygalakturonsäure, welche das Rückgrat des komplexen Moleküls bildet. Daher entwickelte das Team zunächst mehrere Ustilago maydis-Stämme, die unterschiedliche Enzyme für den Abbau von Polygalakturonsäure produzieren und ausscheiden. Dabei untersuchten die Forschenden zum Beispiel das pilzeigene Enzym Endo-Polygalakturonase und bewerteten seine Effektivität. Darüber hinaus übertrugen sie per Gentransfer weitere bereits charakterisierte, potente Enzyme aus anderen Bakterien und Pilzen in ihren Modellorganismus Ustilago maydis. Das Ergebnis: Auch die fremden Enzyme werden erfolgreich von diesem Labor-Pilz produziert und problemlos in das Nährmedium abgegeben. Für die Produktion der bakteriellen Enzyme wird der Umstand ausgenutzt, dass Ustilago maydis über einen unkonventionellen Sekretionsweg verfügt, der diese Enzyme unverändert – also mit vollem Aktivitätspotenzial – in die Umgebung entlässt.
Dieser breit gefächerte Ansatz ermöglichte die Identifizierung von Pilz-Stämmen, die verschiedene aktive pektinolytische Enzyme exportierten. Durch den Einsatz von Mischkulturen, von Stämmen mit komplementären Enzymaktivitäten, wurde abschließend ein effizienter Abbau von Polygalakturonsäure (PolyGalA) zum Baustein Galakturonsäure (GalA) erzielt, die daraufhin vom Pilz verstoffwechselt wurde. Das Projekt legte somit den Grundstein für weitere Schritte in Richtung des Abbaus pektinreicher Biomasse.
Um den Polygalakturonsäureabbau erfolgreich zu etablieren, war der Einsatz von moderner Online-Analytik aus der Bioverfahrenstechnik zur Evaluierung der erstellten Stämme maßgeblich. Dabei wurden die Pilz-Stämme auf Polygalakturonsäure kultiviert und zeitgleich ihre Atmungsrate im Verlauf der Kultivierung ermittelt. Die Auswertung der Daten ermöglichte eine Charakterisierung der einzelnen Stämme in Bezug auf den jeweiligen Substratumsatz und die Enzymaktivität. So konnte eine indirekte Quantifizierung der Polygalakturonsäurekonzentration basierend auf der Atmungsrate erreicht werden. Auch Mischkulturen konnten auf diese Weise effizient analysiert werden.
Weitere Produkte im Fokus
Als Beispiel für ein wertvolles Industrieprodukt fokussierte sich das Forscherteam zunächst auf die organische Säure Itakonat, die von Ustilago maydis natürlicherweise unter Stickstoffmangel produziert wird. Sie ist eine wichtige Plattformchemikalie in der Polymerchemie. Ihr Einsatzfeld reicht von der Produktion von Farben und Lacken über Verdickungsmittel für Fette, Pharmazeutika oder als Herbizid bis hin zu biologisch abbaubaren Polymeren. Die Biosynthese von Itakonat wird durch ein Gencluster reguliert und erwies sich beim Vergleich unterschiedlicher Ustilago maydis-Stämme als stark schwankend. Besonders in dem für die Sekretion von pektinabbauenden Enzymen genutzten Stammhintergrund war nur eine geringe Itakonatproduktion zu beobachten. Durch den Vergleich der biosynthetischen Enzyme auf Genomebene mit verwandten Brandpilzen konnten neue genetische Ansätze entwickelt werden, um diese Schwankungen zu beheben. Dem Team gelang es hierbei, den zentralen Regulator des Genclusters durch einen genetischen Kniff dauerhaft zu aktivieren. Dies erwies sich als hervorragende Stellschraube für ein hohes Grundniveau der Itakonatproduktion. Das Verfahren legt den Grundstein für den angestrebten Bioprozess.
In „PectiLyse“ konnten somit sowohl auf der Ebene des Substratabbaus als auch auf der Ebene der Itakonatproduktion erste grundlegende Schritte auf dem Weg zu einem effizienten Bioprozess etabliert werden. Dies war nur durch ein Team möglich, das in den Bereichen Mikrobiologie, Biotechnologie und Bioingenieurwissenschaften eng zusammenarbeitete. Zukünftig werden die Forscherinnen und Forscher den Pilz weiter für den Abbau von Pektin optimieren. Gleichzeitig arbeiten sie an einem konsolidierten Bioprozess, bei dem aus den frei werdenden fermentierbaren Zuckern weitere wertvolle Moleküle entstehen. Neben Itakonat sind auch andere Produkte wie Biotenside, organische Säuren, Sesquiterpene, die als Duft- und Aromastoffe eingesetzt werden, oder Pharmaproteine denkbar. Die Produktion von Biotensiden wurde im BioSC „FocusLab Bio2“ erfolgreich etabliert. Somit könnte Ustilago maydis basierend auf den interdisziplinären Arbeiten im Rahmen des BioSC zeitnah als flexibler Plattformorganismus für die industrielle Biotechnologie dienen.
Projektleiter
Dr. Kerstin Schipper
Institut für Mikrobiologie, HHU Düsseldorf
Email
Beteiligte Core Groups
Prof. Dr. Michael Feldbrügge, Dr. Kerstin Schipper, Dr. Benedikt Steuten, Dr. Peter Stoffels
Institut für Mikrobiologie, HHU Düsseldorf
Prof. Dr. Lars M. Blank, Prof. Dr. Nick Wierckx1, Dr. Elena von Helden (née Geiser)
ABBt - Angewandte Mikrobiologie, RWTH Aachen
Prof. Dr.-Ing. Jochen Büchs, Dr. Markus Müller, Dr. Tino Schlepütz
AVT - Bioverfahrenstechnik, RWTH Aachen
Projektlaufzeit
01.11.2015 – 31.10.2017
Förderung
PectiLyse ist Teil des NRW-Strategieprojekt BioSC und gefördert vom Ministerium für Kultur und Wissenschaft des Landes Nordrhein-Westfalen.
Publikationen
Geiser, E, Ludwig, F, Zambanini, T, Wierckx, N and Blank, LM (2016). Draft genome sequences of itaconate-producing ustilaginaceae. Genome Announc 4(6).
Geiser, E, Przybilla, SK, Engel, M, Kleineberg, W, Buttner, L, Sarikaya, E, Hartog, TD, Klankermayer, J, Leitner, W, Bolker, M, Blank, LM and Wierckx, N (2016). Genetic and biochemical insights into the itaconate pathway of ustilago maydis enable enhanced production. Metab Eng 38: 427-435.
Geiser, E, Reindl, M, Blank, LM, Feldbrugge, M, Wierckx, N and Schipper, K (2016). Activating intrinsic carbohydrate-active enzymes of the smut fungus ustilago maydis for the degradation of plant cell wall components. Appl Environ Microbiol 82(17): 5174-5185.
_______________________________________________
1 Neue Adresse: IBG-1 Biotechnologie, Forschungszentrum Jülich