
Das FocusLab Bio² zielte auf die Entwicklung eines wettbewerbsfähigen Bioraffinerieprozesses für die Herstellung von biobasierten Tensiden ab. Rhamnolipide (RLs) und Mannosylerythritol-Lipide (MELs) wurden durch rekombinante Stämme von Pseudomonas putida bzw. Ustilago maydis hergestellt. Das Projekt kombinierte die Stammoptimierung mit der Prozessentwicklung sowie mit in-situ-Ansätzen zur Produktrückgewinnung, um den komplexen Prozessanforderungen Rechnung zu tragen. Eine sozioökonomische Bewertung mittels Life cycle assessment begleitete das Prozessdesign bis hin zur Evaluierung im technischen Maßstab. Durch Erschließung neuer Rohstoffquellen, Erhöhung der Ausbeuten und Etablierung neuer analytischer Methoden trug das Projekt dazu bei, die Wettbewerbsfähigkeit von Biotensiden auf dem Markt zu erhöhen.
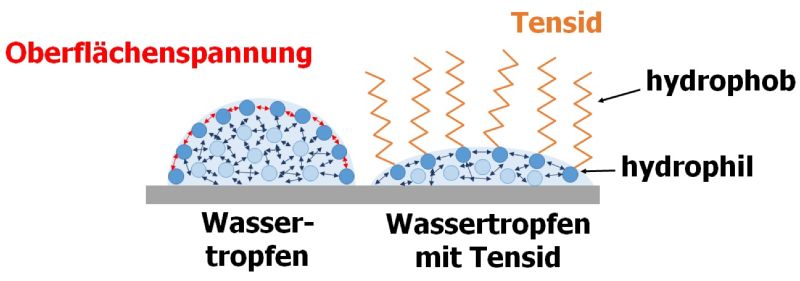
Vollständig biobasierte Tenside („Biotenside“) stellen eine nachhaltige Alternative zu beispielsweise aus Rohöl hergestellten Tensiden dar. (Bio)tenside reduzieren die Oberflächenspannung von Flüssigkeiten oder die Grenzflächenspannung von Dispersionen. Diese Eigenschaft eröffnet vielfältige Anwendungsfelder. So werden Tenside als Detergenzien in Reinigungsmitteln, als Schäumungsmittel bei der Brandbekämpfung aber auch als Emulgatoren in der Lebensmittelindustrie eingesetzt. Dabei sind Biotenside mikrobiellen Ursprungs und lassen sich aus erneuerbaren Rohstoffen herstellen.
Die Produktionskosten von Biotensiden sind höher im Vergleich zu aus Rohöl hergestellten Tensiden. Dies liegt einerseits an der Verwendung teurer Ausgangsstoffe (z. B. aufgereinigte Zucker oder pflanzliche Öle), andererseits an geringen Ausbeuten und Produktionseffizienzen der Mikroorganismen. Außerdem steht die Verwendung von Zuckern oder Ölen als Ausgangsmaterial in Konkurrenz zur Nahrungsmittelproduktion und ist daher kritisch zu bewerten. Die Prozessführung in klassischen Rührkesselbioreaktoren zur Produktion von Biotensiden wird außerdem durch deren inhärente Eigenschaft zur Schaumbildung erschwert. Diese kann zwar durch Zusatz von Antischaummitteln verringert werden, resultiert jedoch in einer komplizierten Aufreinigung.
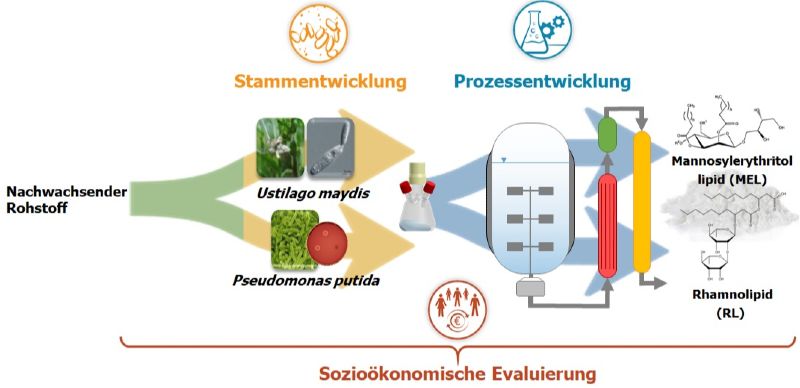
Ziel von Bio2 war daher die Bearbeitung der genannten Herausforderungen in einem ganzheitlichen Ansatz entlang der gesamten Prozesskette. Dazu wurden sowohl Stamm- als auch Prozessentwicklung zeitgleich betrachtet und Prozessstufen miteinander verschaltet. Die Arbeiten wurden kontinuierlich durch eine sozio-ökonomische Analyse begleitet, um den entstehenden Prozess hinsichtlich ökologischer, ökonomischer und sozialer Aspekte zu bewerten und zu verbessern. Als Beispiele für Biotenside wurden mit Hilfe des Bakteriums Pseudomonas putida hergestellte Rhamnolipide (RL) und durch den Pilz Ustilago maydis hergestellte Mannosylerithrytollipide (MEL) ausgewählt. Die grundsätzliche Projektstruktur ist in Abb. 2 dargestellt.
Der ganzheitliche Ansatz war nur in einem stark interdisziplinären Team umsetzbar. Dementsprechend arbeiteten im Bio2-Projekt Naturwissenschaftler/innen und Ingenieur/innen unterschiedlicher Disziplinen eng zusammen.
Wachstum auf nachwachsenden Rohstoffen
Für Pseudomonas putida konnte das Substratspektrum um Xylose und Ethanol erweitert werden. Xylose ist wichtiger Bestandteil von lignocellulosehaltigen Materialien. Dadurch ist es zukünftig möglich, die Rhamnolipidproduktion beispielsweise aus Buchenholzhydrolysat zu untersuchen. So ist eine direkte Verknüpfung zum FocusLab AP³ geschaffen worden. Die Erweiterung des Substratspektrums um Ethanol eröffnet weitere Optionen hinsichtlich der Nutzung alternativer Kohlenstoffquellen.
Für Ustilago maydis konnte die Metabolisierung von Polygalakturonsäure durch die Überexpression von heterologen Polygalakturonasen erreicht werden. Dies ist ein wichtiger Schritt hin zur Nutzung von pektinhaltigen Substraten, zu denen beispielsweise Zuckerrübenschnitzel zählen. Diese sind ein Nebenprodukt aus der Zuckerrübenverarbeitung und stehen somit nicht in Nahrungsmittelkonkurrenz. Außerdem wurde evaluiert, inwieweit die nach dem Prozess verbleibende Biomasse als Fermentationssubstrat eingesetzt werden kann, um die anfallenden Abfallströme weitergehend zu verwerten.
Stammentwicklung zur Steigerung der Produktmengen
Für P. putida wurden zahlreiche Promotorsysteme für die Expression der Rhamnolipidbiosynthesegene adaptiert. Diese erhöhen die genetische Stabilität und ermöglichen die Optimierung der Produktion, beispielsweise durch Anpassung des Induktionszeitpunktes. Außerdem wurde das Genom reduziert, um energieintensive Anwendungen wie beispielsweise die Bildung der Flagellen zu reduzieren. Ein eigens entwickelter Hochdurchsatz Assay im Mikrotiterplattenformat vereinfacht die vergleichende Analyse von Glykolipidproduzenten erheblich.
Bei Verwendung nachwachsender Rohstoffe lässt sich der Stickstoffgehalt nicht beliebig kontrollieren. Mit dem Ziel die Stickstoffabhängigkeit der MEL Produktion in U. maydis zu reduzieren, wurde daher eine 2A Peptid Strategie zur künstlichen Regulation der Biosyntheseschritte etabliert. Zudem konnten wichtige Schritte für die Produktion von reinem MEL-D erzielt werden, indem Seitenprodukte wie Ustilaginsäuren und Itakonsäure eliminiert wurden.
Prozessentwicklung aus ganzheitlicher Perspektive:
Ein neues Konzept zur aeroben Kultivierung – die Membranbegasung – konnte im Rahmen des Projektes entwickelt und zum Patent angemeldet werden. Die Integration der entsprechenden Module in bestehende Bioreaktoren ermöglicht eine weitgehend blasenfreie Begasung des Bioreaktors und vermeidet damit die Schaumbildung im Prozess nahezu vollständig. Die Verschaltung des Membranmoduls mit einer Filtrationsmembran zum Zellrückhalt stellt außerdem die Grundlage für eine in-situ Produktabtrennung dar.
Zur Aufreinigung der Glykolipide aus der Fermentationsbrühe wurden verschiedene Prozessalternativen evaluiert, welche alle eine hohe Reinheit der Produkte bei gleichzeitig hoher Rückgewinnung und damit geringen Produktverlusten erzielen. Hierzu wurden zunächst vorausgewählte Trennoperationen experimentell untersucht sowie modellbasierte Screeningversuche durchgeführt. Auf Basis der Ergebnisse konnten Aufreinigungsprozesse durch Verschaltung der untersuchten Trennoperationen etabliert werden. Die entsprechenden Prozessketten wurden für verschiedene Substrate aus sozioökonomischer Sicht bewertet. Die begleitende Bewertung verschiedener Umweltindikatoren im Rahmen eines Life Cycle Assessment ermöglichte die Identifizierung von wichtigen Stellschrauben zur Prozessoptimierung.
Der zunächst in der Theorie angestrebte ganzheitliche Prozessansatz konnte im Projektverlauf erfolgreich in die Praxis umgesetzt werden. Dies findet unter anderem Ausdruck in einer gemeinsamen Publikation zur Rhamnolipidschiene des Projektes.

Projektleiterin

Dr. Nina Ihling
AVT - Aachener Verfahrenstechnik
RWTH Aachen University
Forckenbeckstraße 51
52074 Aachen, Germany
E-mail: Nina.Ihling@avt.rwth-aachen.de
Phone: +49 241 80-47868
Fax: +49 241 80-22570
Projektlaufzeit
01.05.2017 – 31.12.2020
Förderung
Das Gesamtbudget von Bio² betrug 2,289,709 €. Bio² ist Teil des NRW-Strategieprojekts BioSC und wird gefördert vom Ministerium für Kultur und Wissenschaft des Landes Nordrhein-Westfalen.
Publikationen
Blesken, C. et al. (2020): Genetic cell-surface modification for optimized foam fractionation. Frontiers in Bioengineering and Biotechnology 8
Bator, I. et al. (2020): Killing Two Birds With One Stone – Strain Engineering Facilitates the Development of a Unique Rhamnolipid Production Process. Frontiers in Bioengineering and Biotechnology 8:899.
Kubicki, S. et al. (2020): A Straightforward Assay for Screening and Quantification of Biosurfactants in Microbial Culture Supernatants. Frontiers in Bioengineering and Biotechnology 8:958.
Tiso, T. et al. (2020): Integration of Genetic and Process Engineering for Optimized Rhamnolipid Production Using Pseudomonas putida. Frontiers in Bioengineering and Biotechnology 8: 976.
Müntjes, K., et al. (2020): Establishing Polycistronic gene expression in the model microorganism Ustilago maydis. Frontiers in Microbiology 11:1384
Biselli, A. et al. (2020): Development, evaluation, and optimisation of downstream process concepts for rhamnolipids and 3-(3-hydroxyalkanoyloxy)alkanoic acids. Separation and Purification Technology, 117031.
Bator, I., et al. (2020): Comparison of three xylose pathways in Pseudomonas putida KT2440 for the synthesis of valuable products. Front. Bioeng. Biotechnol. 7: 1-18.
Stoffels, P., et al. (2020): Complementing the intrinsic repertoire of Ustilago maydis for degradation of the pectin backbone polygalacturonic acid. Journal of Biotechnology 307:148-163
Domröse, A., et al. (2019) Pseudomonas putida rDNA is a favored site for the expression of biosynthetic genes. Sci Rep 9, 7028 DOI: 10.1038/s41598-019-43405-1
Otto, M., et al. (2019). Targeting 16S rDNA for Stable Recombinant Gene Expression in Pseudomonas. ACS Synthetic Biology 8(8): 1901-1912
Bollinger, A., et al. (2018). The biotechnological potential of marine bacteria in the novel lineage of Pseudomonas pertucinogena. Microbial Biotechnology 13:19-31.
Hage-Hülsmann, J., et al. (2018). Natural biocide cocktails: Combinatorial antibiotic effects of prodigiosin and biosurfactants. PLoS One 13(7): e0200940