Das Bodenbakterium Pseudomonas putida als nicht-pathogener Vertreter der robusten und vielseitigen Bakterienfamilie der Pseudomonaden ist bekannt als ein exzellenter Ausgangspunkt für die Konstruktion von rekombinanten Produktionsstämmen für Rhamnolipidbiotenside. Auf der anderen Seite fehlen diesem Bakterium von Natur aus Eigenschaften, um für Wachstum und Produktion ein möglichst breites Spektrum an Bioraffinierieprodukten effektiv zu nutzen. Weiterhin wurden bislang überwiegend Plasmide mit starken synthetischen Promotoren zur Expression des für die Produktion von Rhamnolipiden kodierenden Operons zur Integration der Rhamnolipid-Biosynthesegene verwendet. Jedoch gelten im Allgemeinen genomintegrierte Expressionskassetten als besser geeignet zur Konstruktion von stabilen Produktionsstämmen. Im Rahmen von Bio² sollte in komplementären Teilprojekten der native Stoffwechsel von P. putida KT2440 optimiert (Chassis - Abb. 1) sowie die entsprechende rhl-Expressionskassette (Cargo – Abb. 2) für die Produktion von Rhamnolipiden entwickelt werden.
Hierbei wurde die Verstoffwechselung von Xylose und Ethanol als nachwachsende Kohlenstoffquelle adressiert (Abb. 1 A). Die Verwertung von Xylose ermöglicht die Verwendung von kostengünstigem lignocellulosehaltigen Material und erhöht somit die Wertschöpfung eines P. putida-basierten Prozesses. Insgesamt wurden drei verschiedene bakterielle Xylose-Wege – Isomerase-, Weimberg- und Dahms-Weg – plasmidbasiert eingebracht. Die Expression aller drei Wege ermöglichte das Wachstum auf Xylose. Die Implementierung der oxidativen Wege (Weimberg- und Dahms-Weg) erschien dabei als effizienter und führte zu einer hohen Biomasseproduktion. Mit Hilfe von adaptiver Laborevolution konnte die anfängliche Lag-Phase wesentlich verkürzt werden. Ethanol ist ein weiteres interessantes Substrat, da es aus Biomasse hergestellt werden kann und durch die direkte Einschleusung in den zentralen Kohlenstoffmetabolismus in Form von Acetyl-CoA ohne Kohlenstoffverlust besonders effizient nutzbar ist. Die natürliche Fähigkeit von P. putida, Ethanol zu verstoffwechseln konnte durch adaptive Laborevolution deutlich verbessert werden. Für alle diese Chassis konnte gezeigt werden, dass die Produktion auf Basis der alternativen Substrate vergleichbar oder sogar besser ist als mit dem konventionellen Substrat Glukose[1],[2]. Zusätzlich konnte durch weitere Optimierung – bspw. der Deletion energieintensiver Prozesse, wie der Flagellenbiosynthese und –aktivität oder konkurrierender Synthesewege wie der Polyhydroxyalkanoat-Synthese – der Monorhamnolipid-Titer weiter erhöht werden[3] (Abb. 1 B). Durch Metabolic Engineering, hin zu einer verbesserten Bereitstellung der Ausgangsstoffe für die Rhamnolipid-Biosynthese (Rhamnose und Fettsäure in aktivierter Form), konnte die Produktion noch weiter gesteigert werden.
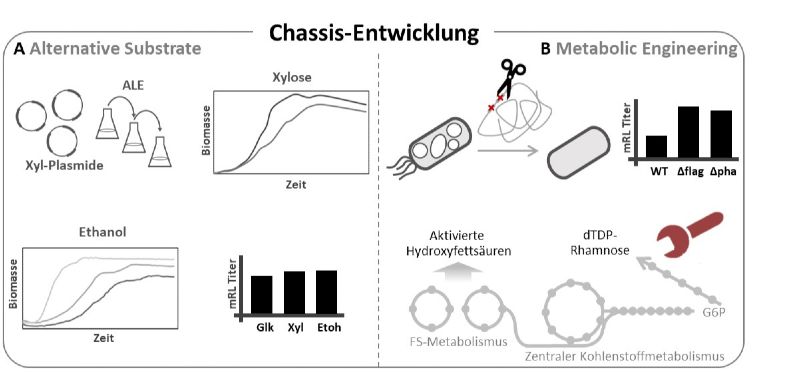
Abb. 1: Chassis-Entwicklung. A – Eine Effektive Metabolisierung von Xylose- und Ethanol wurde durch Kombination von heterologer Expression zusätzlicher Gene und adaptiver Laborevolution erreicht. Es resultierten verschiedene Stämme mit unterschiedlich hohen Wachstumsraten und Monorhamnolipid-Titern auf alternativen Substraten1,2. B - Im Zuge des Metabolic Engineerings wurden Gene für die Flagellen und Polyhydroxyalkanoat-Biosynthese deletiert, wodurch der Monorhamnolipid-Titer gesteigert werden konnte. Zudem wurden Ziele im zentralen Kohlenstoffmetabolismus adressiert, die eine erhöhte Bereitstellung von aktivierter Rhamnose und Fettsäure zur Folge hatten.
Neben der Optimierung des Chassis stand die Entwicklung von Expressionswerkzeugen der nächsten Generation für die Expression der Rhamnolipid-Biosynthesegene im Fokus der Arbeiten von Bio2 (Abb. 2). P. putida KT2440 besitzt diese Gene von Natur aus nicht, was es ermöglicht, deren Expression ohne interferierende natürlich evolvierte Steuerungsprozesse gezielt nach Bedarf zu regulieren.
Zunächst wurde eine neue Variante des Tn7-Transposons konstruiert. Dieses Werkzeug kombiniert die stabile Integration des Biosynthesegene an eine einzigartige Stelle des Genoms mit der Adaptivität der in Zusammenarbeit mit dem BioSC-FL CombiCom entwickelten yTREX toolbox (Abb. 2 A). Dies ermöglichte die effektive Konstruktion eines Sets an Stämmen mit neuen Expressionskassetten und die in dieser Form erstmalig durchgeführten komparativen Expressionsstudien mit zum Einfluss der verschiedenen Promotoren auf die Zielgenexpression, den Rhamnolipid-Titer und die Stammstabilität3 (Abb. 2 B). Hier zeigte sich, dass die Stämme die Fähigkeit zur Bildung von Rhamnolipiden verloren, wenn starke, konstitutive Promotoren verwendet wurden, was auf einen negativen Selektionsdruck durch Rhamnolipid-Produktion hindeutete. Die Induktor-gesteuerten Expressionssysteme, hier erstmalig im Kontext der Rhamnolipid-Biosynthese angewendet, zeigten dagegen eine effiziente Zielgenexpression verbunden mit einer herausragenden Stabilität der Produktionsstämme. Insgesamt führte das Salicylat-induzierbare rhlAB-Expressionssystem zu den besten Produktionseigenschaften. Die Optimierung des Rhamnolipid-Titers und die vollständige Umsetzung der Vorstufe HAA konnte durch Implementierung der Expressionskassette in den genomreduzierten Stammhintergrund sowie durch Co-Integration relevanter Edukt-Synthasen in die Expressionskassette erreicht werden (Abb. 2 C). Abschließend konnte die breitere Anwendbarkeit dieses Expressionssystems durch gezielte Produktion von unterschiedlichen Rhamnolipidvarianten gezeigt werden (Abb. 2 D).
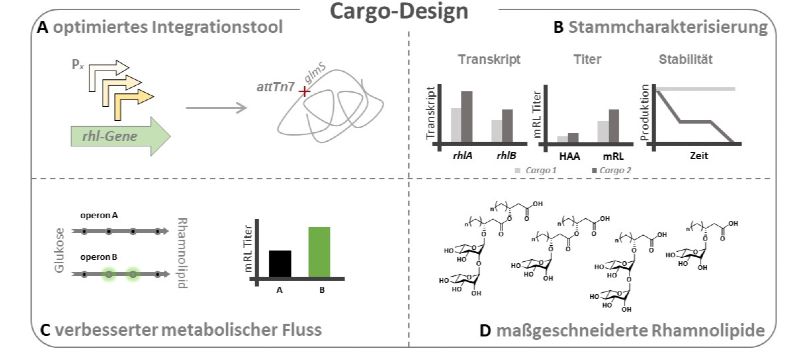
Abb. 2: Cargo-Design. Zur Verbesserung der Expression der Rhamnolipid-Biosynthesegene in P. putida wurden mittels eines neu-entwickelten Integrationstools (A) verschiedene Rhamnolipid-Expressionskassetten mit unterschiedlichen Promotoren konstruiert und charakterisiert3 (B) . In das vielversprechendste System wurden zusätzliche Gene zur Stärkung der des metabolischen Flusses zum Produkt integriert (C), wodurch der Rhamnolipid-Titer weiter gesteigert werden konnte. Dieses System wurde außerdem genutzt, um weitere Rhamnolipidvarianten zu erzeugen (D).
Eine Voraussetzung für die parallele Betrachtung vieler genetisch leicht unterschiedlicher Expressionsstämme zur Optimierung der Rhamnolipid-Produktion waren einfache Methoden, die eine schnelle und zuverlässige Detektion, Quantifizierung und Analyse der Biotensiden zulassen (Abb. 3). Im Rahmen von Bio2 wurden verschiedene Assays zum Hochdurchsatz-Screening entwickelt oder für Rhamnolipide etabliert (Abb. 3 A), wie der atomized-oil und der neu entwickelte VPBO-Assay[4]. Während solche Assays genutzt wurden, um einen Eindruck über die erzielten Titer zu bekommen, gab die entsprechende Analytikplattform Aufschluss über genaue Menge und Zusammensetzung der Rhamnolipide (Abb. 3 B).
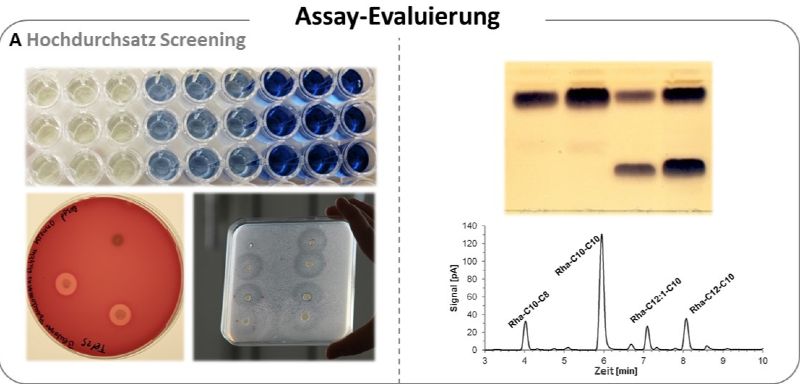
Abb. 3: Detektion von Rhamnolipiden. A – Hochdurchsatz Screening Methoden wie VPBO-Assay[4], Blutagarplatten und Atomized-oil Assay erleichtern die Detektion und Analyse geeigneter Produzenten. B – Methoden zur analytischen Detektion (Dünnschichtchromatographie und Hochleistungsflüssigkeits- chromatographie mit Charged Aerosol-Detektion [HPLC-CAD]) ermöglichen die Identifizierung und Quantifizierung verschiedener Rhamnolipid-Spezies und Kongenere.
[1] https://doi.org/10.3389/fbioe.2019.00480 [2] https://doi.org/10.3389/fbioe.2020.00899
[3] https://doi.org/10.3389/fbioe.2020.00976 [4] https://doi.org/10.3389/fbioe.2020.00958
Prof. Lars Blank
Dr. Till Tiso
Isabel Bator
Institute of Applied Microbiology
RWTH Aachen University
Prof. Karl-Erich Jaeger
Dr. Stephan Thies
Sonja Kubicki
Institute of Molecular Enzyme Technology (IMET)
Heinrich-Heine University Düsseldorf